2. 中国科学院大学,北京 100049
土壤是有生命的,土壤生物赋予土壤的生命属性。土壤生物包括土壤中的微生物(细菌、真菌、古菌和病毒)、藻类、原生生物和土壤动物(线虫、蚯蚓和昆虫等)。土壤生物数量大、种类多、生物量大,是地球上生物多样性的重要组成部分,是联系各个圈层的生命有机体和纽带[1-2]。土壤生物驱动着土壤中几乎所有的生物地球化学循环,在消除土壤污染、改善土壤结构、提升土壤肥力、促进作物健康生长及应对气候变化等方面发挥着重要作用[3],被认为是土壤养分的转化器、污染物的净化器、生态系统的稳定器。土壤生物学研究土壤中生物的组成、多样性与分布格局,土壤生物在元素循环和污染物降解过程中的功能,土壤生物对全球变化与人类干扰的响应与反馈,土壤生物资源及其在生产上的应用等方面。土壤生物学的发展受益于其与土壤学各分支学科、生物学和生态学等多学科的相互交叉、彼此融通,特别是21世纪以来,分子生物学技术的突破与生态学理论的广泛应用为土壤生物学理论的发展提供了强大动力,极大促进了土壤生物学科的发展[1]。同时,在理论和技术发展的支撑下,逐渐形成以调控土壤生物为核心的技术与产品,为维持和促进土壤健康和可持续利用提供了新的途径。伴随着全球气候变化和人类活动的加剧,土壤健康正面临着严重威胁。因此,充分挖掘土壤生物的潜能是保障土壤肥力健康(充足的养分和高效的养分循环)、环境健康和生态健康的关键,进而促进植物健康、农产品健康,最终将服务于人类健康以及人类赖以生存的星球健康。
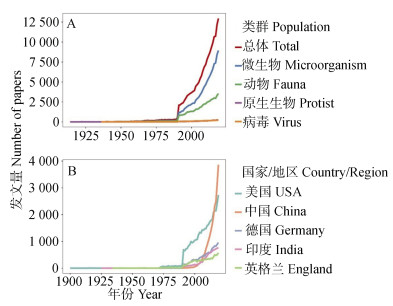
本文基于Web of Science(WoS)核心合集数据库,通过关键词检索(详见附录),统计自1900年至今土壤生物(微生物(不包括病毒)、动物、原生生物和病毒四大类群)学研究的年发文量,并归纳总结了其发展趋势(图 1)。
|
图 1 土壤生物学研究年发文量 Fig. 1 The number of published papers in the study of soil biology |
在20世纪80年代以前,人们对于土壤生物的认识基本停留在形态观察、经典分类及生理学研究,由于受到技术手段的限制,在这一阶段土壤生物学发展较为缓慢。20世纪末期,DNA指纹图谱和基因芯片等分子生物学技术的兴起实现了不依赖于生物的分离培养,而直接在DNA水平上对土壤生物进行分析,开创了土壤生物的分子生态学研究的新时代。自21世纪以来,以现代分子生物学技术(高通量测序和质谱等技术)的突破以及生态学理论在土壤生物学上的广泛应用为标志,我们已经可以从不同水平(DNA、RNA、蛋白质和代谢物)对土壤生物群落进行分析,并逐步形成了系统完整的现代土壤生物学理论体系。随着多组学技术和大数据分析的快速发展以及多学科交叉的促进作用,土壤生物学研究已进入一个崭新的快速发展时期。中国科学院地学部于2012年4月适时启动了“土壤与土壤生物学发展战略研究”项目,该项目又于2012年7月进一步提升为中国科学院和国家自然科学基金委员会联合资助的发展战略研究项目[1]。然而,目前对于土壤生物学的研究主要集中在土壤微生物和动物群落,对于土壤原生生物和病毒的研究仍较少(图 1A)。原生生物作为生物五界之一,是生态系统的重要组分,其研究有助于深入理解土壤生物多样性的产生和维持机制,有助于解析全球变化背景下土壤食物网的结构及功能的演替等重大基础科学问题。值得庆幸的是,近年来我国加大了对这些研究领域的投入。例如,2019年12月30日,中国科学院水生生物研究所等六家科研单位在武汉启动了全球首个“万种原生生物基因组计划(Protist 10000 Genomes Project,简称P10K)”。随着土壤生物学研究的持续推进,特别是对原生生物和病毒的研究,我国在土壤生物学研究领域将有望取得更大进展,进而充分发挥土壤生物学在粮食安全、环境保护、公共卫生和食品安全等诸多核心领域的关键作用。
文献计量结果表明,在土壤生物学研究领域累计发文量排名前五的国家和地区当中,与美国和德国等发达国家相比,我国在该领域的研究起步较晚,始于20世纪80年代(图 1B)。近年来,在中国科学院先导专项“土壤-微生物系统功能及其调控”等重大项目的支持下,我国在土壤生物学研究领域发展迅猛,自2016年以来,我国在土壤生物学领域的年发文量已超越美国,跃居世界第一。从总体上看,我国土壤生物学研究取得了显著进步,在研究的深度与广度上均有不同程度的发展[2]。
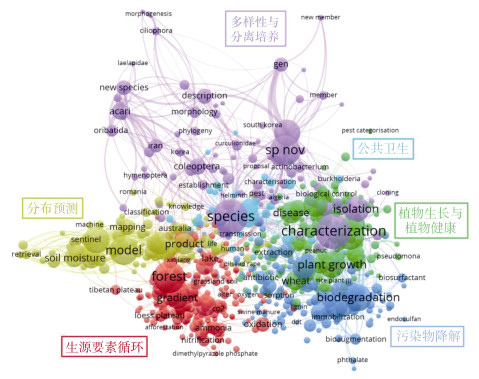
2 学科发展现状本文进一步检索近五年WoS核心合集数据库中的相关文献(包括35 906篇微生物、14 048篇动物、1 792篇原生生物和5 273篇病毒论文),并进行关键词共现网络分析,以反映土壤生物学学科的发展现状。如图 2所示,关键词共现网络主要划分为六个模块:(1)红色模块主要是土壤微生物群落及其介导的生物地球化学循环过程对环境变化的响应;(2)绿色模块主要侧重土壤生物在维持农作物生长与植物健康中的作用;(3)蓝色模块主要研究土壤生物在环境污染物降解中的作用机理;(4)黄色模块主要是不同时空尺度下土壤生物的分布预测;(5)浅蓝色模块主要是土壤生物与公共卫生;(6)紫色模块则聚焦土壤生物的分离培养及形态学鉴定。总体而言,目前土壤生物学研究主要体现在土壤生物多样性与群落结构、土壤生物的功能和土壤生物的调控三个方面。
|
图 2 土壤生物关键词共现网络 Fig. 2 Keywords co-occurrence network of soil organisms |
土壤生物多样性是指土壤中所有的生物种类、它们拥有的基因以及这些生物与环境之间相互作用的多样化程度,是土壤中一切物质转化、能量传递和信息交流的基础,决定着土壤的生态过程、功能与服务[4]。联合国粮食及农业组织(FAO)的《世界土壤宪章》明确指出:地球上至少有四分之一的生物蕴藏于土壤中,它们对物质循环、能量流动和粮食生产等生态系统的功能和服务具有重要的作用。联合国环境规划署(UNEP)和FAO推动成立了全球土壤生物多样性计划(Global Soil Biodiversity Initiative,GSBI),以此提升我们对土壤生物多样性的认知。2014年,第一届国际土壤生物多样性会议在法国巴黎召开。2016年,全球土壤生物多样性图集(Global Soil Biodiversity Atlas)出版。2017年,第二届国际土壤生物多样性会议在中国南京召开。早在2013年,中国生物多样性监测与研究网络(Sino BON)启动建设,建立了包含土壤动物和微生物多样性的监测专项网。土壤生物多样性研究主要包括土壤中生物群落的空间分布及土壤生物对环境变化的响应等。
土壤生物的空间分布主要关注土壤中微生物、原生生物以及无脊椎动物的空间分布格局及其驱动机制,对理解土壤中生物多样性的产生和维持机制具有重要意义。21世纪以来,随着高通量测序技术的突破,土壤微生物空间分布研究得到了空前发展。研究内容涵盖了微生物群落空间分布及其驱动机制、群落构建过程与共存网络、微生物空间分布与生态系统功能的关联以及微生物群落的预测等[5]。例如,Yang等[6]首次发现木本植物系统发育特性对我国东部山地森林土壤真菌群落的空间分布有显著影响。Ladau等[7]利用物种-分布模型绘制了青藏高原土壤微生物的分布图,预测了微生物分布在未来几十年的动态变化。通过构建华北平原麦田土壤细菌与真菌共存网络,耦合土壤功能基因数据,Shi等[8]揭示了核心菌群对土壤功能基因的促进作用。土壤病毒也是土壤生物多样性的重要组成。Wang等[9]揭示了我国东北地区稻田土壤中蓝藻细小病毒的地理分布模式。Schulz等[10]首次对巨型病毒进行全球范围的研究,并初步推断了这些病毒在各生物系统中的空间分布模式和多样性大小等。近年来,土壤原生动物的空间分布也得到了广泛关注。Bates等[11]通过对全球40多处样点的研究,揭示了全球土壤原生动物的分布格局,并发现土壤中原生动物具有较高的多样性。Tedersoo等[12]发现植物多样性对土壤原生动物的分布有重要影响,且这种影响具有生境依赖性。土壤动物作为生态系统物质循环中的重要消费者,在生态系统中起着重要的作用。线虫是地球上最丰富的土壤动物,研究人员通过解析全球6 759份土壤线虫数据,结合气候、土壤和植被等因素,揭示了全球土壤线虫多样性的驱动机制[13]。Phillips等[14]通过对全球57个国家6 928份土壤样品中的蚯蚓研究,发现土著物种在高纬度上具有较高的多样性。尽管土壤生物的空间分布研究取得了一系列进展,但也面临诸多挑战,需要进一步推进高通量测序等技术以及生态学理论在微生物空间分布研究上的运用。
解析土壤生物对环境的响应是我们当前面临的紧迫问题之一。地上植被、土壤含水量、温度和氧化还原状态的改变等均会造成土壤环境的变化,大多数土壤生物会因此进化出相应策略,例如土壤微生物会随着环境压力的增大而发生休眠或者死亡[15]。由于土壤微生物支撑着土壤中其他更高营养级生物的存活,研究者更加关注这一类看不见的群体如何响应环境的变化。大量的研究表明,土壤pH、有机碳含量和盐度等会影响土壤微生物群落结构[16-18],但其影响程度取决于所研究的微生物类群、土壤类型和分析方法等[19]。微生物群落受到多种环境因素的综合调控,我们对于土壤微生物群落对环境变化的响应的认识仍十分有限。此外,地上植被和土壤环境是紧密关联的,土壤环境的变化也会通过影响地上植被而间接影响土壤生物[20-21]。例如,高的植物多样性增加了土壤中的菌根真菌的丰度而减少了植物寄生线虫的丰度[22]。那么,环境变化是直接影响土壤生物还是通过影响地上植被来间接影响土壤生物仍是目前争论的热点议题。
2.2 土壤生物的功能土壤生物在元素的生物化学循环、污染物的降解转化以及土壤免疫抗病等方面均起到举足轻重的作用。土壤生物复杂多样的代谢活动是驱动土壤中各种生源要素(碳氮磷硫铁等)在土壤圈、大气圈、水圈、生物圈间迁移转化的关键动力[23]。因此,解析土壤生源要素生物地球化学循环的生物学机制,是理解土壤生物功能和生物化学过程的关键。很多微生物被发现参与到多种土壤生源要素的循环过程中。例如,参与甲烷代谢过程中的包含甲基辅酶M还原酶基因的广古菌类群可以氧化除甲烷以外的短链烷烃[24]。协助植物从土壤中吸收磷素的丛枝菌根真菌可以在土壤有机碳固持过程中起关键作用[25],在大气CO2浓度升高的背景下通过与腐生微生物相互作用来促进土壤有机碳的分解[26]。在厌氧和缺氧环境中参与脱氮代谢的厌氧氨氧化细菌还能参与金属离子铁的氧化还原过程[27-28]。此外,土壤中高营养级的线虫、蚯蚓等可以通过捕食土壤微生物间接影响元素循环。Bray等[29]和Medina-Sauza等[30]的研究强调了土壤动物对微生物介导的过程具有促进作用,特别是氮矿化和有机质的形成过程。因此,元素的循环有赖于多种土壤生物的协同作用,仅研究特定的微生物功能来理解生源要素的循环是非常片面的。此外,生源要素的循环是土壤微生物群落及其所处环境共同作用的结果[31]。人类活动造成的气候和土地利用方式的改变是如何影响土壤微生物代谢活性,进而影响土壤元素循环依然是一个悬而未决的问题。探索土壤微生物调控的生源要素循环的机制对于预测当前和未来气候变化背景下的生态系统功能至关重要。
除了元素循环,土壤生物也能够降解或转化土壤中的污染物,改善土壤质量。土壤微生物对多环芳烃类有机污染物的降解包括活化-脱芳构化-裂环三个步骤[32]。有氧条件下,细菌和真菌通过羟基化反应激活底物生成邻苯二酚类[33],并由双加氧酶向苯环中插入氧原子,最后通过裂环双加氧酶切割苯环[34]。微生物在厌氧条件下对多环芳烃的降解具有多种途径,在活化步骤中可以通过羟基化、甲基化、磷酸化、羧基化和富马酸化等途径激活底物[35],根据激活方式的差异,脱芳构化和裂环反应需要与之对应的水解酶的参与[32]。此外,真菌还能够通过胞外分泌的木质素水解酶(漆酶、锰过氧化物酶等),非特异地降解包括多环芳烃在内的许多大分子[36]。不同于有机污染物,微生物对重金属污染的去除机制主要包括表面吸附、转运吸收和价态改变等作用[37]。微生物细胞壁上存在大量的羟基、巯基和羧基基团,很容易通过静电吸附、表面络合等作用与金属离子发生表面吸附[38],从而降低土壤中的金属离子浓度和运动性。微生物也能够通过胞外酶或胞内酶与金属离子发生氧化还原反应,改变其化合价降低毒性,例如汞抗性细菌能够将Hg2+还原为毒性较低的Hg单质[39]。此外,微生物也能通过细胞膜上的转运蛋白、铁载体和金属硫蛋白等高效地结合金属离子,将其跨膜转运至细胞质中,通过细胞壁的螯合固定作用沉淀金属离子,或将其储存在细胞空泡中[40]。近年来,研究人员已发现了多种具有污染修复潜力的土壤微生物类群。例如,假单胞菌属的细菌对重金属有极高的抗性,能够高效地去除土壤中的Cd、Cr等重金属离子[41-42]。假单胞菌属和芽胞杆菌属中的菌株已被用于修复芴和菲等有机污染物[43]。此外,土壤中植物生长促生菌(Plant Growth Promoting Rhizobacteria,PGPR)还能够通过与地上植物构建共生关系,提高植物的抗逆性和生物量,间接提高修复效力[44]。污染土壤的生物修复具有高效、节能、环境安全等优点,因此挖掘更多潜在生物降解菌并评估其在土壤中的修复效率是今后污染土壤修复技术研究的热点。
对于土壤免疫抗病而言,土壤中功能微生物的活动所带来的对土传病害的防御机制被称作是土壤免疫;通过调控土壤功能微生物来提高土壤的抗逆性和恢复力对农业的可持续发展具有重要意义[45-46]。类比动物免疫,土壤免疫也分为能够快速响应,非特异性的普通免疫和需要响应时间并对特定的病原体具有记忆的特异性免疫。土壤微生物助力地上植物抗病主要表现在三个方面:(1)依据求救假说(Cry-for-Help Hypothesis),植物在受到病原菌攻击时能招募有益的微生物来对抗病原菌,并形成土壤免疫记忆有益于下一代植物抗病[47-48];(2)土壤微生物刺激植物的免疫系统,诱导植物启动系统抗性从而保护植物免受多种病原体的侵害[49-50];(3)病毒溶解病原菌或造成病原菌突变,从而降低病原菌的侵染能力[51]。因此,“操纵”微生物群落来抑制植物病害将是未来研究的热点问题。
2.3 土壤生物的调控土壤中汇聚的土壤动物和微生物各类群之间相互依赖、共存、竞争、捕食等关系构成的土壤微食物网结构是土壤生态功能的基础,紧密调控着陆地生态系统的养分流动和物质循环过程[52]。土壤微食物网营养结构按物质分解速率由快到慢分为细菌能量通道、植物能量通道和真菌能量通道[53]。食物网中各类生物群落之间“牵一发,而动全身”。研究表明,微食物网结构的变化或顶端捕食者的增加(减少)对土壤功能潜力的影响比生物多样性损失带来的影响更大[54]。因此,正向调控土壤生物群落结构、多样性、微食物网相互关系等有利于促进土壤养分元素循环,维持生态系统健康、稳定和可持续性。越来越多的研究表明,不同生态系统具有不同的微食物网集群。例如,草原生态系统的土壤食物网以真菌为基础,农田生态系统则是以细菌为基础;土壤微食物网对干旱逆境的恢复力稳定性和抵抗力稳定性会受到不同土地利用方式的影响[55]。此外,病毒作为微生物群落的重要成员,影响土壤微生物的死亡率,碳、氮等营养循环以及土壤微食物网动态[56]。近年来,关于土壤病毒(噬菌体,RNA病毒)群落的研究日益增多,通过稳定性同位素探针技术定向研究病毒与细菌及与植物的相互关系将有利于进一步完善土壤微食物网框架。由于土壤微食物网结构复杂多样,以往研究主要根据显微镜观察计数来定量原生动物、线虫等的生物量,或者通过磷脂脂肪酸(PLFA)定量分析细菌、真菌的生物量,今后需要利用多组学技术与生物相互关系网络模型来解析土壤微食物网的结构与功能。
除了从宏观角度调控整体土壤生物群落及其相互关系之外,还可以通过添加微生物菌剂来调节土壤生物群落结构,从而改善土壤养分状况和植物健康。例如,添加微生物菌剂可以直接或间接控制土著病原菌的入侵和发作,缓解作物连作障碍,防控常见作物疾病,活化土壤磷钾养分等。同时,在无菌条件下人工构建微生物组可以用以研究特定微生物群体营养机理及竞争关系。例如,Niu等[57]在7种单菌构建的合成细菌群落中找到了抑制晚疫病的关键微生物菌种,并进一步验证了组合菌群对病原菌的抑制作用强于单一菌的效果。Wei等[58]通过人工构建暴露于入侵病原菌的细菌群落模型,揭示了细菌群落与病原微生物的潜在资源竞争模式是通过降低病原菌的入侵率和限制病原菌的生长实现的。Castrillo等[59]利用35株合成微生物菌群发现并验证了磷元素缺乏条件下,微生物群落效应不仅激活了植物对磷酸盐应激反应基因,还直接抑制了植物免疫基因的表达,从而建立了植物营养与免疫之间的分子机制。此外,通过构建简易微生物菌群还可以验证土壤微生物生态理论,解释生态现象,揭示生理机制等[60],从而实现对土壤生物的靶向调控。
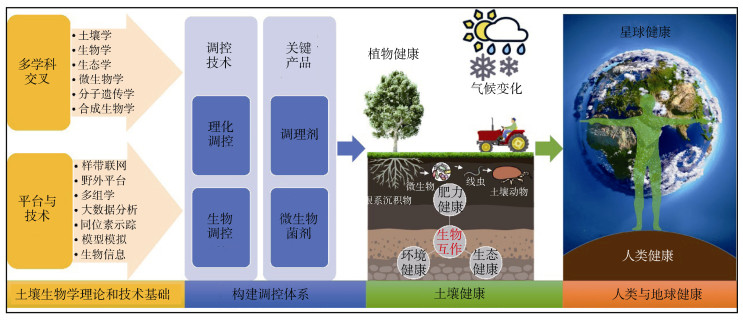
3 学科发展趋势 3.1 在理论上的发展趋势随着土壤生物学与生态学、微生物学及土壤学等学科的不断交叉融合,野外控制试验和样带联网等试验平台的建立、多组学和大数据分析等技术的突破,土壤生物学在理论与应用上均有了极大的发展(图 3)。目前,土壤生物学理论主要包含生物多样性的产生与维持机制、生物生态过程与演变规律以及生物功能特性与生态系统服务关系等方面。
|
图 3 土壤生物学分支学科发展趋势 Fig. 3 The development trend of the subdiscipline of soil biology |
土壤生物多样性的产生与维持机制关注土壤生物本身,以解释土壤中有哪些生物类群、它们的多样性是如何产生和维持的,并受什么因素驱动为基本内容。目前,宏观生态学上较为完善的理论如岛屿生物地理学理论[61]、集合种群理论[62]和生态学代谢理论[63]等均已被用来解释土壤生物多样性的产生和维持机制。岛屿生物地理学理论强调随着岛屿面积的增加和隔离程度(通常以岛屿到邻近陆地的距离表示)的下降,岛屿上的生物多样性显著上升。该理论首次从动态平衡的角度阐述了生物多样性与生境面积及隔离程度的关系,提出岛屿上的物种多样性取决于新物种的迁入和原物种的灭绝。经过近半世纪的发展[64],该理论已成功应用在对土壤生物多样性分布规律的研究中[65-66]。借助虚拟的岛屿系统(树冠层土壤),Wardle等[67]发现随着岛屿尺寸的增大,土壤中微小节肢动物的多样性显著上升。近期,我国学者利用杭州千岛湖不同大小的岛屿作为模式系统发现岛屿面积越小,其土壤细菌和真菌的多样性越低,有力地证明了该理论的普适性[68]。不同的土壤生物多样性理论并非相互排斥[69],未来不同理论框架的叠加与融合将在更大程度上推进我们对土壤生物多样性产生与维持机制的理解。
土壤生物生态过程与演变规律则更加关注在全球变化背景下,如气候变暖、人类活动和生物入侵对土壤生物的群落结构和种间关系的影响。20世纪50年代,MacArthur[70]首次提出任意一个群落的物种多样性应与它的稳定性之间存在相关关系,其稳定性取决于物种的多少和种间互作。目前,生态学理论诸如中度干扰假说[71]、群落中性理论和生态位理论[72]、多样性与稳定性的关系[73]等已被运用在土壤生物的生态学研究中。贺纪正等[74]对土壤生态系统微生物多样性与其稳定性的关系展开了论述,提出土壤微生物系统是一个动态变化的自组织系统,通过遗传维持其组成和结构的相对稳定,通过变异适应外界干扰,共同形成土壤生态系统的抵抗力和恢复力。Hanson等[75]提出任何的微生物生物地理分布格局均由四类基本过程决定,包括选择、漂变、扩散和变异,四类过程相互作用,在生态和进化尺度上塑造着微生物的时空格局。通过建立完备的分析方法和理论框架[76-78],研究人员可以将微生物群落的构建过程定量区分到随机性过程和确定性过程[79],甚至更为细分的过程[80],完成从格局理论到过程理论的升华。未来以系统和网络理论观点为指引[81-82],整合研究土壤食物网中各营养级生物的生态过程与演变规律将为该方面理论发展提供新的动力。
土壤生物功能特性与生态系统服务关系以土壤生物功能特性对整个生态系统的增益和福祉为根本出发点。其理论涉及Janzen-Connell法则[83-84]、植物-土壤反馈调节[85]、多样性-生产力关系[86]等。早在20世纪末,研究人员就通过两个独立且互补的模拟实验,证明了地下丛枝菌根真菌的多样性是维持地上植物多样性和生态系统功能的重要因素[87]。以古田山24公顷大样地连续9年的监测数据为基础,研究人员发现树木的同种负密度制约效应与土壤真菌类群有关,快速积累病原真菌的树木种群往往受负密度制约效应的调节较强,而拥有外生菌根的树木种群受负密度制约效应的调节较弱,因此,土壤病原真菌和外生菌根真菌共同调控森林植物物种组成[88]。通过对青藏高原大尺度的生态调查,研究人员发现土壤真菌多样性与植物多样性强耦合,而与地上植物生产力无直接联系[89]。近期,研究人员发现长期施肥管理下的土壤环境已不能主动选择与固氮活性密切相关的关键固氮菌群,由此造成土壤固氮功能的不可逆丢失[90]。因此,耦联地上、地下生物多样性及其与生态系统服务功能的关系是该方向理论发展的重要趋势。如何将土壤微生物个体功能属性的研究整合在大生态模型中则是未来该理论模型构建的难点和热点[91-92]。
3.2 在应用上的发展趋势在土壤生物学理论和技术的驱动下,土壤生物学研究成果已经迈入向实际应用转化的重要时期,土壤生物类群及其与植物(根系)以共存网络或者食物链等多营养级形式相互关联,在相对稳定的土壤环境中,逐渐形成了以土壤生物互作及其与土壤环境和植物根系互作为核心的调控体系(图 3)。
一方面,土壤生物之间以多营养级微食物网模式共存[93-94],其相互作用的过程中涉及营养依赖、生物膜形成、分子通讯、传播功能以及真菌与细菌内共生等互动机制[95]。因此,确定食物网中多种生物群落共现和潜在交互模式的主要驱动因素,以及它们与生态系统功能的关联,可以帮助我们构建以土壤生物或土壤环境(如理化性状、养分增减)为核心的土壤生物调控技术(图 3)。
另一方面,植物以及土壤生物可以通过产生信号和高能量分子作为生态介质,选择性地激活生物种群并触发启动效应,导致特定有机基质的降解、合成和隔离[96]。植物完全依靠每个细胞的先天免疫能力来应对环境中的各种微生物,它们通过细胞外识别微生物和宿主损伤相关的分子模式导致第一层诱导防御,被称为模式触发免疫(pattern-triggered immunity,PTI)。植物免疫保护植物免受病虫害在很大程度上是通过这些过程实现的,使得植物生存的核心取决于有益微生物和病原微生物与宿主之间的信号交流[97]。因此,识别植物性状、免疫和土壤生物(主要是土壤微生物类群)之间的关联,有助于选育特定植物性状来富集特异微生物,定向调控土壤生物与植物之间的互作关系,从而使得土壤生物与植物的相互影响进入良性循环,促进土壤和植物的整体健康。
近期,全国人大代表沈仁芳研究员表示“土壤是植物生产的载体,同时也是生态环境的基本要素。贫瘠的土壤无法保障食物的营养和产量,污染的土壤影响人居环境和农产品安全”。健康的土壤不仅要求较高的肥力,还需要清洁的土壤环境。利用土壤生物治理和改善土壤环境,是未来土壤生物学发展的重大需求。基于上述对土壤生物调控技术原理的认知,加强对土壤生物(特别是微生物)功能发挥的研究,开发一系列促生、抗病、抗逆、污染修复等功能产品(如复合菌剂),并与调控技术相结合,构建完善的土壤生物调控体系(图 3)。目前,应用于作物栽培和生产的微生物菌剂在减少化学肥料和农药的使用、提高土壤免疫力、保障农产品产量与品质方面均被验证具有巨大的应用前景[98]。土壤生物理论与技术的发展将使调控技术和关键菌剂产品的应用提高到新的水平,但是在现阶段仍然需要进一步测试和验证。
土壤生物作为农业生产、医药卫生和环境保护等领域的核心生物资源之一,以其丰富的物种和功能多样性,在应对粮食、能源、生态与环境等方面均具有巨大潜力,并成为新一轮科技革命的战略高地。土壤生物学的发展同时依赖于理论发展和技术进步,基于对土壤生物功能及其生物过程的认知,选择合适的技术手段,构建以生物良性互作为核心的土壤生物调控体系,有针对性地开展恢复、维持、促进土壤健康等多方面的管理和调控,最终达到土壤自然资源(肥力)、环境和生态综合属性健康的目标。
4 学科展望我国有着世界上最庞大的人口,可耕地面积却极为有限。伴随着经济的快速发展,土壤出现了肥力退化、污染加重、土传病害增加等诸多问题,严重影响了土壤健康,并引发一系列环境生态问题。土壤生物学理论与技术的快速发展将为解决这些问题提供强有力的支撑,但也面临诸多挑战。现代土壤生物学学科应以土壤生物多样性为基础,以土壤-生物-环境的统一体为研究对象,以土壤生物的生态过程与服务功能为最终目标,构建起包括各土壤生物类群在内的,整合地上与地下、结构与功能、生态与进化的多维度的学科体系。该学科体系应以土壤生物多样性的产生和维持机制、土壤生物生态过程机理以及土壤生物的生态系统服务功能为主线不断扩展、相互交融、纵深发展。现代土壤生物学学科的创建和完善应充分考虑当今生态环境问题,重视与生产实践相结合,为我国的土壤健康和安全提供坚实保障。从国家需求与学科发展出发,土壤生物学今后应加强以下几方面的研究:
(1)土壤生物多样性及其资源挖掘。土壤中蕴藏着极其丰富的生物资源,解析土壤生物多样性及其时空分布格局是保护、开发及利用这些生物资源的前提。因此,未来需通过组学技术(宏基因组、宏转录组、宏代谢组和宏蛋白质组等)研究土壤生物群落的空间分布规律、时间动态变化、群落构建机制,以更好地理解土壤生物多样性的形成与维持机制。同时,还需要通过分离培养、细胞分选等手段识别并获得土壤中有特定功能的菌株,并进行功能验证,开发具有特定功能的微生物菌种资源。进一步通过大规模分离培养手段与现代生物工程技术,研发可以保存并利用的复合生物菌剂,以实现土壤生物关键产品的应用。
(2)土壤生物群落与功能对环境变化的响应与反馈。气候变化、环境污染以及人为扰动会直接或间接地影响土壤生物及其相关的地下生态过程和功能,反之,土壤生物会通过其参与的地下生态过程对全球变化产生正向或负向的反馈,加强或削弱全球变化给生态系统带来的影响。未来需要重点研究环境变化下土壤生物群落的演替规律和生态过程,揭示土壤生物与地上植被的耦合机制,为预测环境变化下陆地生态系统的演变提供参考。
(3)土壤生物功能的调控理论与应用。土壤中的生物类群以群落形式共存,形成微生物-植物的共生或寄生关系、组建植物根系-微生物-动物食物链等多营养级的复杂结构,并受到土壤理化性状、气候环境等非生物因素的影响。今后需进一步阐明土壤生物、植物根系以及环境之间的互作关系,量化生物互作中的影响因素,以形成土壤生物的调控理论体系;进一步通过调控土壤理化性状和植物性状、施用复合菌剂、构建人工简易微生物组等方式来形成土壤生物调控的技术体系,共同促进土壤与植物健康。
| [1] |
中国科学院, 国家自然科学基金委员会. 中国学科发展战略·土壤生物学. 北京: 科学出版社, 2016. Chinese Academy of Sciences, National Natural Science Foundation of China. China's discipline development strategy·Soil Biology (In Chinese). Beijing: Science Press, 2016. (  0) 0) |
| [2] |
宋长青, 冷疏影, 谭文峰, 等. 土壤科学三十年:从经典到前沿. 北京: 商务印书馆, 2016. Song C Q, Leng S Y, Tan W F, et al. Thirty years of Soil Science: From the classics to the frontiers (In Chinese). Beijing: The Commercial Press, 2016. (  0) 0) |
| [3] |
张俊伶, 张江周, 申建波, 等. 土壤健康与农业绿色发展:机遇与对策. 土壤学报, 2020, 57(4): 783-796. Zhang J L, Zhang J Z, Shen J B, et al. Soil health and agriculture green development: Opportunities and challenges (In Chinese). Acta Pedologica Sinica, 2020, 57(4): 783-796. (  0) 0) |
| [4] |
Bardgett R D, van der Putten W H. Belowground biodiversity and ecosystem functioning . Nature, 2014, 515(7528): 505-511. DOI:10.1038/nature13855
(  0) 0) |
| [5] |
褚海燕, 冯毛毛, 柳旭, 等. 土壤微生物生物地理学:国内进展与国际前沿. 土壤学报, 2020, 57(3): 515-529. Chu H Y, Feng M M, Liu X, et al. Soil Microbial Biogeography: Recent advances in China and research frontiers in the world (In Chinese). Acta Pedologica Sinica, 2020, 57(3): 515-529. (  0) 0) |
| [6] |
Yang T, Tedersoo L, Soltis P S, et al. Phylogenetic imprint of woody plants on the soil mycobiome in natural mountain forests of eastern China . The ISME Journal, 2019, 13(3): 686-697. DOI:10.1038/s41396-018-0303-x
(  0) 0) |
| [7] |
Ladau J, Shi Y, Jing X, et al. Existing climate change will lead to pronounced shifts in the diversity of soil prokaryotes . mSystems, 2018, 3: e00167-18. DOI:10.1128/mSystems.00167-18
(  0) 0) |
| [8] |
Shi Y, Delgado-Baquerizo M, Li Y T, et al. Abundance of kinless hubs within soil microbial networks are associated with high functional potential in agricultural ecosystems . Environment International, 2020, 142: 105869. DOI:10.1016/j.envint.2020.105869
(  0) 0) |
| [9] |
Wang G, Liu J, Yu Z, et al. Unique distribution of cyanobacterial podoviruses and their potential hosts in a paddy field of northeast China . FEMS Microbiology Ecology, 2014, 90(1): 331-334.
(  0) 0) |
| [10] |
Schulz F, Roux S, Paez-Espino D, et al. Giant virus diversity and host interactions through global metagenomics . Nature, 2020, 578(7795): 432-436. DOI:10.1038/s41586-020-1957-x
(  0) 0) |
| [11] |
Bates S T, Clemente J C, Flores G E, et al. Global biogeography of highly diverse protistan communities in soil . The ISME Journal, 2013, 7(3): 652-659. DOI:10.1038/ismej.2012.147
(  0) 0) |
| [12] |
Tedersoo L, Bahram M, Cajthaml T, et al. Tree diversity and species identity effects on soil fungi, protists and animals are context dependent . The ISME Journal, 2016, 10(2): 346-362. DOI:10.1038/ismej.2015.116
(  0) 0) |
| [13] |
van den Hoogen J, Geisen S, Routh D, et al. Soil nematode abundance and functional group composition at a global scale . Nature, 2019, 572(7768): 194-198. DOI:10.1038/s41586-019-1418-6
(  0) 0) |
| [14] |
Phillips H R P, Guerra C A, Bartz M L C, et al. Global distribution of earthworm diversity . Science, 2019, 366(6464): 480-485. DOI:10.1126/science.aax4851
(  0) 0) |
| [15] |
Jansson J K, Hofmockel K S. Soil microbiomes and climate change . Nature Reviews Microbiology, 2020, 18(1): 35-46. DOI:10.1038/s41579-019-0265-7
(  0) 0) |
| [16] |
Shen C, Xiong J, Zhang H, et al. Soil pH drives the spatial distribution of bacterial communities along elevation on Changbai Mountain . Soil Biology and Biochemistry, 2013, 57: 204-211. DOI:10.1016/j.soilbio.2012.07.013
(  0) 0) |
| [17] |
Sul W J, Asuming-Brempong S, Wang Q, et al. Tropical agricultural land management influences on soil microbial communities through its effect on soil organic carbon . Soil Biology and Biochemistry, 2013, 65: 33-38. DOI:10.1016/j.soilbio.2013.05.007
(  0) 0) |
| [18] |
Zhang K, Shi Y, Cui X, et al. Salinity is a key determinant for soil microbial communities in a desert ecosystem . mSystems, 2019, 4(1): e00225-00218. DOI:10.1128/mSystems.00225-18
(  0) 0) |
| [19] |
Fierer N. Embracing the unknown: Disentangling the complexities of the soil microbiome . Nature Reviews Microbiology, 2017, 15(10): 579. DOI:10.1038/nrmicro.2017.87
(  0) 0) |
| [20] |
Wubs E J, van der Putten W H, Mortimer S R, et al. Single introductions of soil biota and plants generate long-term legacies in soil and plant community assembly . Ecology Letters, 2019, 22(7): 1145-1151. DOI:10.1111/ele.13271
(  0) 0) |
| [21] |
Pugnaire F I, Morillo J A, Peñuelas J, et al. Climate change effects on plant-soil feedbacks and consequences for biodiversity and functioning of terrestrial ecosystems . Science Advances, 2019, 5(11): eaaz1834. DOI:10.1126/sciadv.aaz1834
(  0) 0) |
| [22] |
Bennett J A, Koch A M, Forsythe J, et al. Resistance of soil biota and plant growth to disturbance increases with plant diversity . Ecology Letters, 2020, 23(1): 119-128. DOI:10.1111/ele.13408
(  0) 0) |
| [23] |
Sanyal S K, Shuster J, Reith F. Cycling of biogenic elements drives biogeochemical gold cycling . Earth-Science Reviews, 2019, 190: 131-147. DOI:10.1016/j.earscirev.2018.12.010
(  0) 0) |
| [24] |
Evans P N, Boyd J A, Leu A O, et al. An evolving view of methane metabolism in the archaea . Nature Reviews Microbiology, 2019, 17(4): 219-232. DOI:10.1038/s41579-018-0136-7
(  0) 0) |
| [25] |
Averill C, Turner B L, Finzi A C. Mycorrhiza-mediated competition between plants and decomposers drives soil carbon storage . Nature, 2014, 505(7484): 543-545. DOI:10.1038/nature12901
(  0) 0) |
| [26] |
Cheng L, Booker F L, Tu C, et al. Arbuscular mycorrhizal fungi increase organic carbon decomposition under elevated CO2 . Science, 2012, 337(6098): 1084-1087. DOI:10.1126/science.1224304
(  0) 0) |
| [27] |
Ferousi C, Lindhoud S, Baymann F, et al. Iron assimilation and utilization in anaerobic ammonium oxidizing bacteria . Current Opinion in Chemical Biology, 2017, 37: 129-136. DOI:10.1016/j.cbpa.2017.03.009
(  0) 0) |
| [28] |
Kuypers M M, Marchant H K, Kartal B. The microbial nitrogen-cycling network . Nature Reviews Microbiology, 2018, 16(5): 263. DOI:10.1038/nrmicro.2018.9
(  0) 0) |
| [29] |
Bray N, KaoKniffin J, Frey S D, et al. Soil macroinvertebrate presence alters microbial community composition and activity in the rhizosphere . Frontiers in Microbiology, 2019, 10: 256. DOI:10.3389/fmicb.2019.00256
(  0) 0) |
| [30] |
Medina-Sauza R M, Álvarez-Jiménez M, Delhal A, et al. Earthworms building up soil microbiota, a review . Frontiers in Environmental Science, 2019, 7: 81. DOI:10.3389/fenvs.2019.00081
(  0) 0) |
| [31] |
Rousk J, Bengtson P. Microbial regulation of global biogeochemical cycles . Frontiers in Microbiology, 2014, 5: 103.
(  0) 0) |
| [32] |
Ladino-Orjuela G, Gomes E, da Silva R, et al. Metabolic pathways for degradation of aromatic hydrocarbons by bacteria[M]//de Voogt W. Reviews of environmental contamination and toxicology volume 237. Cham: Springer International Publishing, 2016: 105-121.
(  0) 0) |
| [33] |
Huijbers M M E, Montersino S, Westphal A H, et al. Flavin dependent monooxygenases . Archives of Biochemistry and Biophysics, 2014, 544: 2-17. DOI:10.1016/j.abb.2013.12.005
(  0) 0) |
| [34] |
Fetzner S. Ring-cleaving dioxygenases with a cupinfold . Applied and Environmental Microbiology, 2012, 78(8): 2505-2514. DOI:10.1128/AEM.07651-11
(  0) 0) |
| [35] |
Heider J. Adding handles to unhandy substrates: Anaerobic hydrocarbon activation mechanisms . Current Opinion in Chemical Biology, 2007, 11(2): 188-194. DOI:10.1016/j.cbpa.2007.02.027
(  0) 0) |
| [36] |
Deshmukh R, Khardenavis A A, Purohit H J. Diverse metabolic capacities of fungi for bioremediation . Indian Journal of Microbiology, 2016, 56(3): 247-264. DOI:10.1007/s12088-016-0584-6
(  0) 0) |
| [37] |
Ayangbenro A S, Babalola O O. A new strategy for heavy metal polluted environments: A review of microbial biosorbents . International Journal of Environmental Research and Public Health, 2017, 14(1): 94. DOI:10.3390/ijerph14010094
(  0) 0) |
| [38] |
Gadd G M. Biosorption: Critical review of scientific rationale, environmental importance and significance for pollution treatment . Journal of Chemical Technology and Biotechnology, 2009, 84(1): 13-28. DOI:10.1002/jctb.1999
(  0) 0) |
| [39] |
Wu G, Kang H, Zhang X, et al. A critical review on the bio-removal of hazardous heavy metals from contaminated soils: Issues, progress, eco-environmental concerns and opportunities . Journal of Hazardous Materials, 2010, 174(1): 1-8.
(  0) 0) |
| [40] |
Choudhary M, Kumar R, Datta A, et al. Bioremediation of heavy metals by microbes[M]// Arora S, Singh A K, Singh Y P. Bioremediation of salt affected soils: An indian perspective. Cham: Springer International Publishing, 2017: 233-255.
(  0) 0) |
| [41] |
Chellaiah E R. Cadmium(heavy metals)bioremediation by Pseudomonas aeruginosa: A minireview . Applied Water Science, 2018, 8(6): 154. DOI:10.1007/s13201-018-0796-5
(  0) 0) |
| [42] |
Gupta P, Rani R, Chandra A, et al. Potential applications of Pseudomonas sp.(strain cpsb21)to ameliorate Cr6+ stress and phytoremediation of tannery effluent contaminated agricultural soils[ . Scientific Reports, 2018, 8(1): 4860. DOI:10.1038/s41598-018-23322-5
(  0) 0) |
| [43] |
Rabodonirina S, Rasolomampianina R, Krier F, et al. Degradation of fluorene and phenanthrene in PAHs-contaminated soil using pseudomonas and bacillus strains isolated from oil spill sites . Journal of Environmental Management, 2019, 232: 1-7.
(  0) 0) |
| [44] |
Azubuike C C, Chikere C B, Okpokwasili G C. Bioremediation techniques-classification based on site of application: Principles, advantages, limitations and prospects . World Journal of Microbiology and Biotechnology, 2016, 32(11): 180. DOI:10.1007/s11274-016-2137-x
(  0) 0) |
| [45] |
Raaijmakers J M, Mazzola M. Soil immune responses . Science, 2016, 352(6292): 1392-1393. DOI:10.1126/science.aaf3252
(  0) 0) |
| [46] |
Wang L, Li X. Steering soil microbiome to enhance soil system resilience . Critical Reviews in Microbiology, 2019, 45(5/6): 743-753.
(  0) 0) |
| [47] |
Bakker P A, Pieterse C M, de Jonge R, et al. The soil-borne legacy . Cell, 2018, 172(6): 1178-1180. DOI:10.1016/j.cell.2018.02.024
(  0) 0) |
| [48] |
Yuan J, Zhao J, Wen T, et al. Root exudates drive the soil-borne legacy of aboveground pathogen infection . Microbiome, 2018, 6(1): 1-12. DOI:10.1186/s40168-017-0383-2
(  0) 0) |
| [49] |
Teixeira P J P, Colaianni N R, Fitzpatrick C R, et al. Beyond pathogens: Microbiota interactions with the plant immune system . Current Opinion in Microbiology, 2019, 49: 7-17. DOI:10.1016/j.mib.2019.08.003
(  0) 0) |
| [50] |
Wang K-D, Borrego E J, Kenerley C M, et al. Oxylipins other than jasmonic acid are xylem-resident signals regulating systemic resistance induced by trichodermavirens in maize . The Plant Cell, 2020, 32(1): 166-185.
(  0) 0) |
| [51] |
Wang X, Wei Z, Yang K, et al. Phage combination therapies for bacterial wilt disease in tomato . Nature Biotechnology, 2019, 37(12): 1513-1520. DOI:10.1038/s41587-019-0328-3
(  0) 0) |
| [52] |
Sackett T E, Classen A T, Sanders N J. Linking soil food web structure to above- and belowground ecosystem processes: A meta-analysis . Oikos, 2010, 119(12): 1984-1992. DOI:10.1111/j.1600-0706.2010.18728.x
(  0) 0) |
| [53] |
Wardle D A, Verhoef H A, Clarholm M. Trophic relationships in the soil microfood-web: Predicting the responses to a changing global environment . Global Change Biology, 1998, 4(7): 713-727. DOI:10.1046/j.1365-2486.1998.00206.x
(  0) 0) |
| [54] |
Barnes A D, Jochum M, Mumme S, et al. Consequences of tropical land use for multitrophic biodiversity and ecosystem functioning . Nature Communications, 2014, 5: 5351. DOI:10.1038/ncomms6351
(  0) 0) |
| [55] |
De Vries F T, Liiri M E, Bjørnlund L, et al. Land use alters the resistance and resilience of soil food webs to drought . Nature Climate Change, 2012, 2(4): 276. DOI:10.1038/nclimate1368
(  0) 0) |
| [56] |
Emerson J B. Soil viruses: A new hope . mSystems, 2019, 4(3): e00120-00119.
(  0) 0) |
| [57] |
Niu B, Paulson J N, Zheng X, et al. Simplified and representative bacterial community of maize roots . Proceedings of the National Academy of Sciences, 2017, 114(12): E2450-E2459. DOI:10.1073/pnas.1616148114
(  0) 0) |
| [58] |
Wei Z, Yang T, Friman V P, et al. Trophic network architecture of root-associated bacterial communities determines pathogen invasion and plant health . Nature Communications, 2015, 6(1): 8413. DOI:10.1038/ncomms9413
(  0) 0) |
| [59] |
Castrillo G, Teixeira P J P L, Paredes S H, et al. Root microbiota drive direct integration of phosphate stress and immunity . Nature, 2017, 543(7646): 513-518. DOI:10.1038/nature21417
(  0) 0) |
| [60] |
Vorholt J A, Vogel C, Carlström C I, et al. Establishing causality: Opportunities of synthetic communities for plant microbiome research . Cell Host and Microbe, 2017, 22(2): 142-155. DOI:10.1016/j.chom.2017.07.004
(  0) 0) |
| [61] |
MacArthur R H, Wilson E O. The theory of island biogeography[M]. Princeton University Press, 1967.
(  0) 0) |
| [62] |
Baguette M. The classical metapopulation theory and the real, natural world: A critical appraisal . Basic and Applied Ecology, 2004, 5(3): 213-224. DOI:10.1016/j.baae.2004.03.001
(  0) 0) |
| [63] |
Brown J H, Gillooly J F, Allen A P, et al. Toward a metabolic theory of ecology . Ecology, 2004, 85(7): 1771-1789. DOI:10.1890/03-9000
(  0) 0) |
| [64] |
Patiño J, Whittaker R J, Borges P A V, et al. A roadmap for island biology: 50 fundamental questions after 50 years of the theory of island biogeography . Journal of Biogeography, 2017, 44(5): 963-983. DOI:10.1111/jbi.12986
(  0) 0) |
| [65] |
Peay K, Garbelotto M, Bruns T. Evidence of dispersal limitation in soil microorganisms: Isolation reduces species richness on mycorrhizal tree islands . Ecology, 2010, 91: 3631-3640. DOI:10.1890/09-2237.1
(  0) 0) |
| [66] |
Davison J, Moora M, Öpik M, et al. Microbial island biogeography: Isolation shapes the life history characteristics but not diversity of root-symbiotic fungal communities . The ISME Journal, 2018, 12(9): 2211-2224. DOI:10.1038/s41396-018-0196-8
(  0) 0) |
| [67] |
Wardle D A, Yeates G W, Barker G M, et al. Island biology and ecosystem functioning in epiphytic soil communities . Science, 2003, 301(5640): 1717-1720. DOI:10.1126/science.1087809
(  0) 0) |
| [68] |
Li S-p, Wang P, Chen Y, et al. Island biogeography of soil bacteria and fungi: Similar patterns, but different mechanisms . The ISME Journal, 2020. DOI:10.1038/s41396-020-0657-8
(  0) 0) |
| [69] |
Thakur M P, Phillips H R P, Brose U, et al. Towards an integrative understanding of soil biodiversity . Biological Reviews, 2020, 95(2): 350-364. DOI:10.1111/brv.12567
(  0) 0) |
| [70] |
MacArthur R. Fluctuations of animal populations and a measure of community stability . Ecology, 1955, 36: 533-536. DOI:10.2307/1929601
(  0) 0) |
| [71] |
Connell J H. Diversity in tropical rain forests and coral reefs . Science, 1978, 199(4335): 1302-1310. DOI:10.1126/science.199.4335.1302
(  0) 0) |
| [72] |
牛克昌, 刘怿宁, 沈泽昊, 等. 群落构建的中性理论和生态位理论. 生物多样性, 2009, 17(6): 579-593. Niu K C, Liu Y N, Shen Z H, et al. Community assembly: The relative importance of neutral theory and niche theory (In Chinese). Biodiversity Science, 2009, 17(6): 579-593. (  0) 0) |
| [73] |
黄建辉, 韩兴国. 生物多样性和生态系统稳定性. 生物多样性, 1995, 3(1): 31-37. Huang J H, Han X G. Biodiversity and ecosystem stability (In Chinese). Biodiversity Science, 1995, 3(1): 31-37. (  0) 0) |
| [74] |
贺纪正, 李晶, 郑袁明. 土壤生态系统微生物多样性-稳定性关系的思考. 生物多样性, 2013, 21(4): 412-421. He J Z, Li J, Zheng Y M. Thoughts on the microbial diversity-stability relationship in soil ecosystems (In Chinese). Biodiversity Science, 2013, 21(4): 412-421. (  0) 0) |
| [75] |
Hanson C A, Fuhrman J A, Horner-Devine M C, et al. Beyond biogeographic patterns: Processes shaping the microbial landscape . Nature Reviews Microbiology, 2012, 10(7): 497-506. DOI:10.1038/nrmicro2795
(  0) 0) |
| [76] |
Stegen J C, Lin X, Fredrickson J K, et al. Quantifying community assembly processes and identifying features that impose them . The ISME Journal, 2013, 7(11): 2069-2079. DOI:10.1038/ismej.2013.93
(  0) 0) |
| [77] |
Dini-Andreote F, Stegen J C, van Elsas J D, et al. Disentangling mechanisms that mediate the balance between stochastic and deterministic processes in microbial succession . Proceedings of the National Academy of Sciences, 2015, 112(11): E1326-E1332. DOI:10.1073/pnas.1414261112
(  0) 0) |
| [78] |
Stegen J C, Lin X, Fredrickson J K, et al. Estimating and mapping ecological processes influencing microbial community assembly . Frontiers in Microbiology, 2015, 6: Article 370.
(  0) 0) |
| [79] |
Shi Y, Li Y, Xiang X, et al. Spatial scale affects the relative role of stochasticity versus determinism in soil bacterial communities in wheat fields across the North China Plain . Microbiome, 2018, 6(1): 27. DOI:10.1186/s40168-018-0409-4
(  0) 0) |
| [80] |
Feng M, Tripathi B M, Shi Y, et al. Interpreting distance-decay pattern of soil bacteria via quantifying the assembly processes at multiple spatial scales . MicrobiologyOpen, 2019, 8(9): e00851.
(  0) 0) |
| [81] |
Layeghifard M, Hwang D M, Guttman D S. Disentangling interactions in the microbiome: A network perspective . Trends in Microbiology, 2017, 25(3): 217-228. DOI:10.1016/j.tim.2016.11.008
(  0) 0) |
| [82] |
Castledine M, Sierocinski P, Padfield D, et al. Community coalescence: An eco-evolutionary perspective . Philosophical Transactions of the Royal Society B: Biological Sciences, 2020, 375(1798): 20190252. DOI:10.1098/rstb.2019.0252
(  0) 0) |
| [83] |
Janzen D H. Herbivores and the number of tree species in tropical forests . The American Naturalist, 1970, 104(940): 501-528. DOI:10.1086/282687
(  0) 0) |
| [84] |
Connell J H. On the role of natural enemies in preventing competitive exclusion in some marine animals and in rain forest trees[M]//den Boer P J, Gradwell G R. Dynamics of numbers in populations. PUDOC, Wageningen, the Netherlands, 1971: 298-312.
(  0) 0) |
| [85] |
van der Putten W H, Bardgett R D, Bever J D, et al. Plant-soil feedbacks: The past, the present and future challenges . Journal of Ecology, 2013, 101(2): 265-276. DOI:10.1111/1365-2745.12054
(  0) 0) |
| [86] |
Tilman D. The ecological consequences of changes in biodiversity: A search for general principles . Ecology, 1999, 80: 1455-1474.
(  0) 0) |
| [87] |
van der Heijden M G A, Bruin S D, Luckerhoff L, et al. A widespread plant-fungal-bacterial symbiosis promotes plant biodiversity, plant nutrition and seedling recruitment . The ISME Journal, 2016, 10(2): 389-399. DOI:10.1038/ismej.2015.120
(  0) 0) |
| [88] |
Chen L, Swenson N G, Ji N, et al. Differential soil fungus accumulation and density dependence of trees in a subtropical forest . Science, 2019, 366(6461): 124-128. DOI:10.1126/science.aau1361
(  0) 0) |
| [89] |
Yang T, Adams J M, Shi Y, et al. Soil fungal diversity in natural grasslands of the Tibetan Plateau: Associations with plant diversity and productivity . New Phytologist, 2017, 215(2): 756-765. DOI:10.1111/nph.14606
(  0) 0) |
| [90] |
Fan K, Delgado-Baquerizo M, Guo X, et al. Suppressed N fixation and diazotrophs after four decades of fertilization . Microbiome, 2019, 7(1): 143. DOI:10.1186/s40168-019-0757-8
(  0) 0) |
| [91] |
Crowther T W, van den Hoogen J, Wan J, et al. The global soil community and its influence on biogeochemistry . Science, 2019, 365(6455).
(  0) 0) |
| [92] |
Zanne A E, Abarenkov K, Afkhami M E, et al. Fungal functional ecology: Bringing a trait-based approach to plant-associated fungi . Biological Reviews, 2020, 95(2): 409-433. DOI:10.1111/brv.12570
(  0) 0) |
| [93] |
Gessner M O, Swan C M, Dang C K, et al. Diversity meets decomposition . Trends in Ecology and Evolution, 2010, 25(6): 372-380. DOI:10.1016/j.tree.2010.01.010
(  0) 0) |
| [94] |
Nielsen U N, Ayres E, Wall D H, et al. Soil biodiversity and carbon cycling: A review and synthesis of studies examining diversity-function relationships . European Journal of Soil Science, 2011, 62(1): 105-116.
(  0) 0) |
| [95] |
Hassani M A, Duran P, Hacquard S. Microbial interactions within the plant holobiont . Microbiome, 2018, 6(1): 58. DOI:10.1186/s40168-018-0445-0
(  0) 0) |
| [96] |
Lavelle P, Spain A, Blouin M, et al. Ecosystem engineers in a self-organized soil: A review of concepts and future research questions . Soil Science, 2016, 181(3/4): 91-109. DOI:10.1097/SS.0000000000000155
(  0) 0) |
| [97] |
Ding Y, Gardiner D M, Xiao D, et al. Regulators of nitric oxide signaling triggered by host perception in a plant pathogen . Proceedings of the National Academy of Sciences, 2020, 117(20): 11147-11157. DOI:10.1073/pnas.1918977117
(  0) 0) |
| [98] |
白洋, 钱景美, 周俭民, 等. 农作物微生物组:跨越转化临界点的现代生物技术. 中国科学院院刊, 2017, 32(3): 260-265. Bai Y, Qian J M, Zhou J M, et al. Crop Microbiome: Breakthrough technology for agriculture (In Chinese). Bulletin of Chinese Academy of Sciences, 2017, 32(3): 260-265. (  0) 0) |
2. University of Chinese Academy of Sciences, Beijing 100049, China
 2020, Vol. 57
2020, Vol. 57

